Kohlendioxidmessung der Messstation Wasserkuppe
Stand: 27.04.2021
 |
|---|
| Kohlendioxidmessung der Messstation Wasserkuppe |
Der Boden als Kohlenstoffspeicher ist keine Konstante, sondern reagiert äußerst dynamisch auf veränderte Konzentrationen von Treibhausgasen in der Atmosphäre. Darum ist es wichtig den Kohlendioxidgehalt zu verfolgen. Das Hessische Landesamt für Naturschutz, Umwelt und Geologie, liefert aktuelle Messwerte der Kohlendioxid-Konzentrationen von zwei Stationen in Hessen. Diese befinden sich in Linden und Wasserkuppe.1
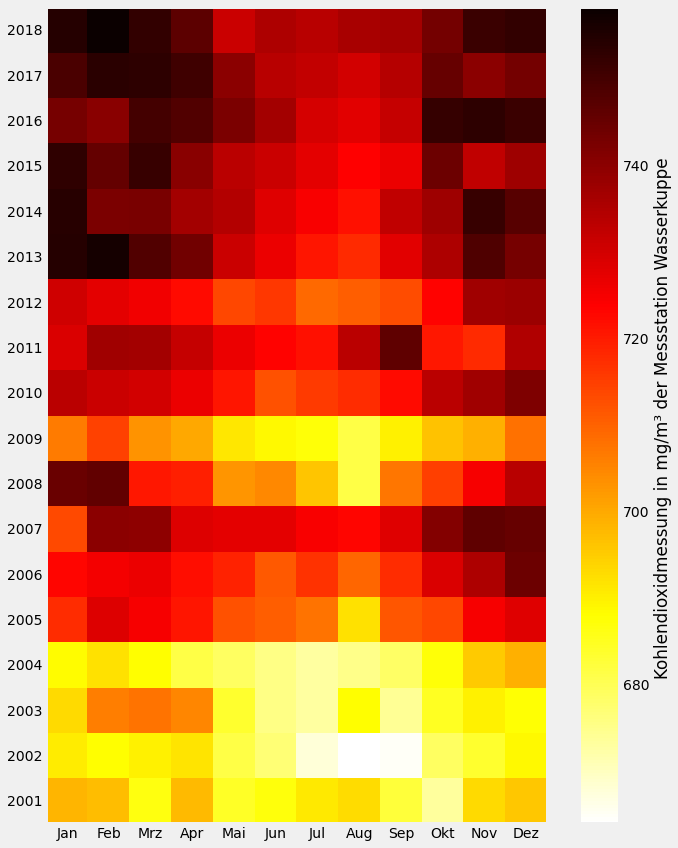
Für die Jahre 2001-2018, siehe obige Abbildung, wurden die Daten nach Monat gruppiert. Jedes Element der Matrix stellt den monatlichen Mittelwert der Kohlendioxidmessung der Messstation Wasserkuppe dar. Die Angaben als Massenkonzentrationen in $mg/m^3$ gelten nur für die bestimmten Bedingungen von Druck und Temperatur. Daten als Volumenmischungsverhältnisse in ppm sind unabhängig von Druck und Temperatur. 2
In der Abbildung erkennt man den Photosyntheseeffekt der Vegetation. In den Wintermonaten ist der Kohlendioxidgehalt der Atmosphäre höher, da eine Assimilation kaum vorhanden ist. Bei der Assimilation werden aufgenommene, fremde anorganische und organische Stoffe aus der Umwelt in Bestandteile des Organismus umgewandelt, meistens unter Energiezufuhr. Ein Beispiel dafür ist die Bildung von Glucose.
\[6 H_2O + 6 CO_2 → C_6 H_{12} O_6 + 6 O_2\]Durch die Photosynthese von Landpflanzen werden in den weiteren Monaten Kohlendioxid entzogen, dies kann man gut in den Monaten von Mai bis September erkennen, dort ist die Kohlendioxidmessung am geringsten.
Der Mittelwert ist von 2001-2004 konstant und ab 2005 gestiegen. Bedingt durch umfangreiche anthropogene Freisetzung wird der natürliche Treibhauseffekt verstärkt, welches eine Klimaänderung zur Folge hat.
Der Datensatz
Der Datensatz stammt vom Hessisches Landesamt für Naturschutz, Umwelt und Geologie (HLNUG). Dieser wurde von folgender Webseite runtergeladen. http://www.hlnug.de/messwerte/datenportal/messstelle/2/1/0801/7,11,20
Folgendes wurde gewählt: Luft, Luftmessnetz, Wasserkuppe. Mit den drei ausgewählten Parametern Kohlendioxid (CO₂), Luftdruck, Temperatur und dem Stundenmittelwert. Temperatur und Luftdruck sind notwendig um die Messwerte in das Volumenmischungsverhältnis ppm umzurechnen. Der Download fand am 05.06.2020 statt, für diesem Zeitraum: 05.07.2000 - 04.06.2020.
 |
|---|
| Standort der Messstation Wasserkuppe |
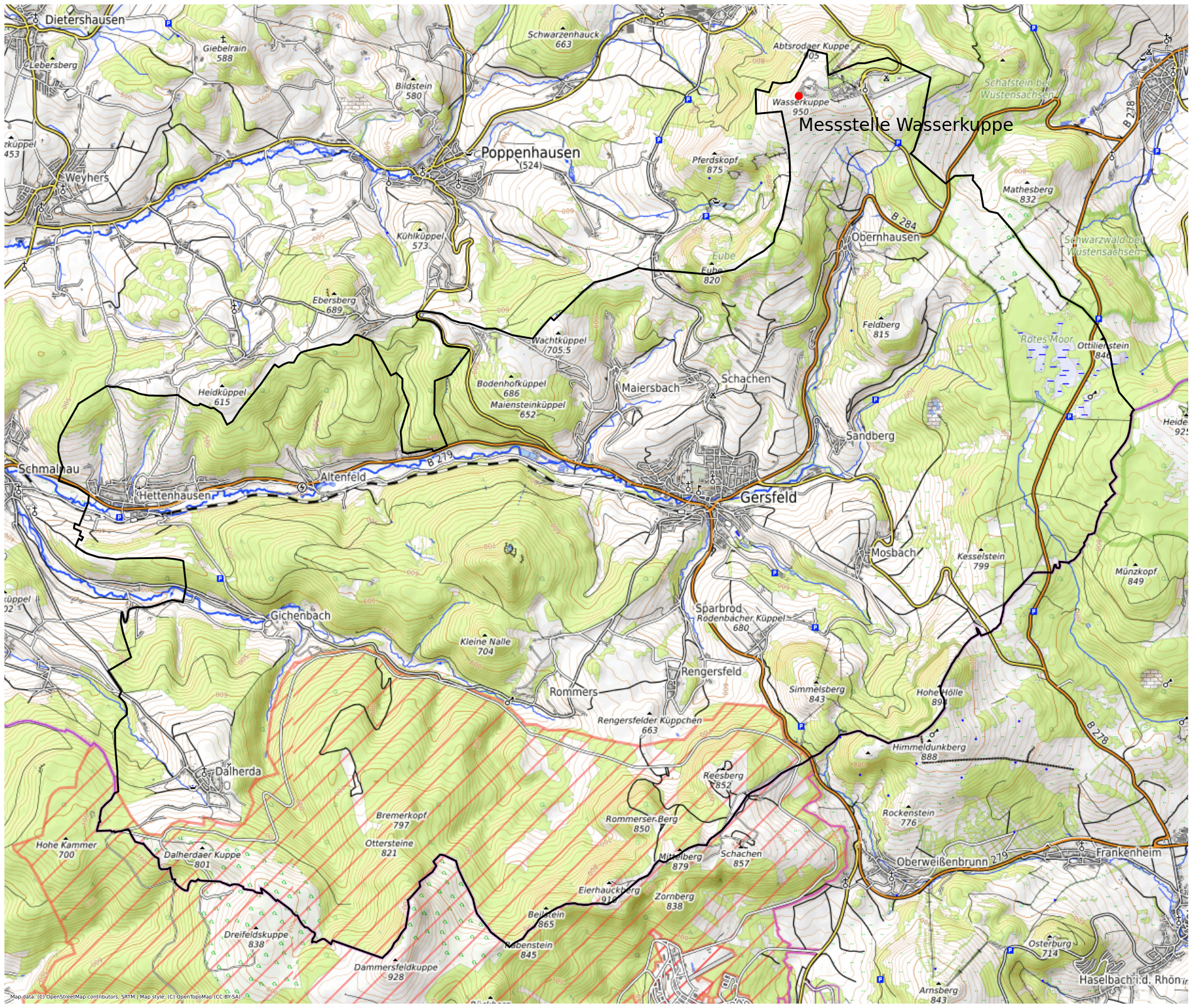
Messstellenstandort Wasserkuppe mit Geopandas
Welchen Einfluss hat der Messstellenstandort Wasserkuppe auf die Messdaten? Vor allem die anthropogen Einflüsse der näheren Umgebung. Die Visualisierung wird mit geopandas umgesetzt. Geopandas ist eine Pythonbibliothek für die Arbeit mit Geodaten. Für eine visuelle Eingrenzung liefert eine Shapefile, ein Format für vektorielle Geodaten, Polygondaten mit Bundesländer und Postleitzahlengebiete. Im weiteren Verlauf wird der Umgang mit dem Koordinatenbezugssystem beschrieben, den Installationsblauf von Geopandas gezeigt und eine OpenStreetMap als Basiskarte eingebunden.
Das Koordinatenreferenzsystem oder Koordinatenbezugsystem (KBS), engl. coordinate reference system, international mit CRS abgekürzt, beschreibt die Lage eines Koordinatensystems zur Angabe einer Position auf der Erde.
EPSG-Codes
Der EPSG-Code ist ein System weltweit eindeutiger, 4- bis 5-stelliger Schlüsselnummern für Koordinatenreferenzsysteme und andere geodätische Datensätze, wie Referenzellipsoide oder Projektionen.
| Code | Koordinatenreferenzsystem | Bemerkung |
|---|---|---|
| 4326 | WGS-84 / Geographische Koordinaten | weltweites System für GPS-Geräte, OpenStreetMap Datenbank |
| 3857 | WGS 84 / Pseudo-Mercator | Google Maps, OpenStreetMap |
| 31467 | DHDN / Gauß-Krüger Zone 3 | passend für Baden-Württemberg und Hessen. |
Installation
Es wurde Python 3.7 genutzt. Die folgende Installationsreihenfolge ist wichtig. Microsoft Visual C++ 14.0 oder höher wird benötigt. Dieses kann unter https://visualstudio.microsoft.com/de/visual-cpp-build-tools/ runtergeladen werden.
- pip install numpy
- pip install pandas
- pip install shapely
- pip install pipwin
- pipwin install gdal
- pipwin install fiona
- pip install pyproj
- pip install six
- pip install rtree
pip install geopandas
- pip install matplotlib
- pip contextily —> lieferte den Fehler: A GDAL API version must be specified. Provide a path to gdal-config using a GDAL_CONFIG environment variable or use a GDAL_VERSION environment variable.
Deswegen:
- conda install contextily –channel conda-forge
Shapefile Deutschland
Die benötigte Shapefile wurde von folgender Seite runtergeladen: www.suche-postleitzahl.org/downloads. Die folgende Seite war dabei sehr hilfreich.3
- plz-gebiete.shp: Die Datei enthält die Polygone der einzelnen Postleitzahlenbereiche
- zuordnung_plz_ort.csv: Die zugehörige Postleitzahl als Bezeichner für Ort und Bundesland. Das Dateiformat ist im CSV-Format.
import geopandas as gpd
import pandas as pd
import numpy as np
import matplotlib.pyplot as plt
plt.style.use('fivethirtyeight')
%matplotlib inline
Die Postleitzahlen müssen als String gelesen werden. Sonst wird eine 01 beginnende PLZ mit 1 geparst. Die shapefile wird geladen und das CRS ausgegeben. Alle vier Dateien mit den Endungen, .dbf , prj , shp , shx sollten im selben Ordner sein.
dtl_shapefile_df = gpd.read_file('plz-gebiete.shp', dtype={'plz': str}, encoding="utf-8")
dtl_shapefile_df
| plz | note | geometry | |
|---|---|---|---|
| 0 | 52538 | 52538 Gangelt, Selfkant | POLYGON ((5.86632 51.05110, 5.86692 51.05124, ... |
| 1 | 47559 | 47559 Kranenburg | POLYGON ((5.94504 51.82354, 5.94580 51.82409, ... |
| 2 | 52525 | 52525 Waldfeucht, Heinsberg | POLYGON ((5.96811 51.05556, 5.96951 51.05660, ... |
| 3 | 52074 | 52074 Aachen | POLYGON ((5.97486 50.79804, 5.97495 50.79809, ... |
| 4 | 52531 | 52531 Übach-Palenberg | POLYGON ((6.01507 50.94788, 6.03854 50.93561, ... |
| ... | ... | ... | ... |
| 8720 | 02899 | 02899 Ostritz, Schönau-Berzdorf | POLYGON ((14.85296 51.06854, 14.85449 51.06859... |
| 8721 | 02929 | 02929 Rothenburg/O.L. | POLYGON ((14.85491 51.32895, 14.85608 51.33004... |
| 8722 | 02827 | 02827 Görlitz | POLYGON ((14.91168 51.14243, 14.91571 51.14571... |
| 8723 | 02828 | 02828 Görlitz | POLYGON ((14.93413 51.16084, 14.93451 51.16123... |
| 8724 | 02826 | 02826 Görlitz | POLYGON ((14.95374 51.14703, 14.95393 51.14814... |
8725 rows × 3 columns
dtl_shapefile_df.crs
{'init': 'epsg:4326'}
plz_ort_df = pd.read_csv(
'zuordnung_plz_ort.csv',
sep=',',
dtype={'plz': str}
)
plz_ort_df.drop('osm_id', axis=1, inplace=True)
plz_ort_df.head()
| ort | plz | bundesland | |
|---|---|---|---|
| 0 | Aach | 78267 | Baden-Württemberg |
| 1 | Aach | 54298 | Rheinland-Pfalz |
| 2 | Aachen | 52062 | Nordrhein-Westfalen |
| 3 | Aachen | 52064 | Nordrhein-Westfalen |
| 4 | Aachen | 52066 | Nordrhein-Westfalen |
Verbinde die .shape-Datei mit der csv-Datei, nutze dabei die Postleitzahlen. Dies ist ein typischer Excel sverweis.
deutschland_df = pd.merge(
left=dtl_shapefile_df,
right=plz_ort_df,
on='plz',
how='inner'
)
deutschland_df.drop(['note'], axis=1, inplace=True)
deutschland_df.head()
| plz | geometry | ort | bundesland | |
|---|---|---|---|---|
| 0 | 52538 | POLYGON ((5.86632 51.05110, 5.86692 51.05124, ... | Gangelt | Nordrhein-Westfalen |
| 1 | 52538 | POLYGON ((5.86632 51.05110, 5.86692 51.05124, ... | Selfkant | Nordrhein-Westfalen |
| 2 | 47559 | POLYGON ((5.94504 51.82354, 5.94580 51.82409, ... | Kranenburg | Nordrhein-Westfalen |
| 3 | 52525 | POLYGON ((5.96811 51.05556, 5.96951 51.05660, ... | Heinsberg | Nordrhein-Westfalen |
| 4 | 52525 | POLYGON ((5.96811 51.05556, 5.96951 51.05660, ... | Waldfeucht | Nordrhein-Westfalen |
Messstellenstandort Wasserkuppe
import shapely
import contextily as ctx
wasserkuppe_df = deutschland_df.query(('plz == "36129"'))
wasserkuppe_df = wasserkuppe_df.to_crs(epsg=3857)
df = pd.DataFrame({'city': ['Wasserkuppe'],
'latitude': [50.49768412],
'longitude': [9.9358506]})
gdf = gpd.GeoDataFrame(df.drop(['latitude', 'longitude'], axis=1),
crs = {'init': 'epsg:4326'},
geometry = [shapely.geometry.Point(xy)
for xy in zip(df.longitude, df.latitude)])
gdf = gdf.to_crs(epsg = 3857)
print(gdf)
fig = plt.figure(figsize = (15,15))
ax = plt.subplot()
ax.text(x = 1106053.829, y = 6532916.278 - 715, s ='Messstelle Wasserkuppe', size = 18)
wasserkuppe_df = wasserkuppe_df.plot(color='none',edgecolor='black', linewidth=3, ax = ax)
ax.set_axis_off()
gdf.plot(ax = wasserkuppe_df, marker = 'o', color = 'red', markersize = 150)
ctx.add_basemap(ax = ax, source=ctx.providers.OpenTopoMap)
city geometry
0 Wasserkuppe POINT (1106053.829 6532916.278)
Der rote schraffierte Bereich ist das Sperrgebiet Truppenübungsplatz Wildflecken.
Einfluss des Messstellenstandort auf die Messdaten
Die Lichter der Erde bei Nacht sind hauptsächlich vom Menschen gemacht. Dieses wird genutzt um die nährere Umgebung des Standortes auf die anthropogenen Einflüsse einzuschätzen. Hierfür werden Satellitenbilder genutzt. Vom Visible-Infrared-Imaging-Radiometer-Suite-Instrument (VIIRS) auf dem Suomi-NPP-Satelliten, der am 28. Oktober 2011 von NASA und NOAA (National Oceanic and Atmospheric Administration) gestartet worden ist.
Das VIIRS-Instrument wurde speziell entwickelt, um die Erde tagsüber statt nachts zu beobachten. Seine Empfindlichkeit reicht aus, um das Licht eines einzelnen Schiffes auf der Erdoberfläche zu erfassen.4
wasserkuppe_df = deutschland_df
wasserkuppe_df = wasserkuppe_df.to_crs(epsg=3857)
df = pd.DataFrame({'city': ['Wasserkuppe'],
'latitude': [50.49768412],
'longitude': [9.9358506]})
gdf = gpd.GeoDataFrame(df.drop(['latitude', 'longitude'], axis=1),
crs = {'init': 'epsg:4326'},
geometry = [shapely.geometry.Point(xy)
for xy in zip(df.longitude, df.latitude)])
gdf = gdf.to_crs(epsg = 3857)
print(gdf)
fig = plt.figure(figsize = (20,20))
ax = plt.subplot()
ax.text(x = 1106053.829 - 47150, y = 6532916.278 + 5915, s ='Messstelle Wasserkuppe', size = 28, color = 'white')
wasserkuppe_df = wasserkuppe_df.plot(color='none',edgecolor='gray', linewidth=0, ax = ax)
ax.set_axis_off()
gdf.plot(ax = wasserkuppe_df, marker = 'o', color = 'red', markersize = 150)
ctx.add_basemap(ax = ax, source=ctx.providers.NASAGIBS.ViirsEarthAtNight2012)
city geometry
0 Wasserkuppe POINT (1106053.829 6532916.278)

wasserkuppe_df = deutschland_df.query(('bundesland == "Hessen"'))
wasserkuppe_df = wasserkuppe_df.to_crs(epsg=3857)
df = pd.DataFrame({'city': ['Wasserkuppe'],
'latitude': [50.49768412],
'longitude': [9.9358506]})
gdf = gpd.GeoDataFrame(df.drop(['latitude', 'longitude'], axis=1),
crs = {'init': 'epsg:4326'},
geometry = [shapely.geometry.Point(xy)
for xy in zip(df.longitude, df.latitude)])
gdf = gdf.to_crs(epsg = 3857)
print(gdf)
fig = plt.figure(figsize = (25,25))
ax = plt.subplot()
ax.text(x = 1106053.829 - 47150, y = 6532916.278 + 5915, s ='Messstelle Wasserkuppe', size = 18, color = 'white')
wasserkuppe_df = wasserkuppe_df.plot(color='none',edgecolor='gray', linewidth=1, ax = ax)
ax.set_axis_off()
gdf.plot(ax = wasserkuppe_df, marker = 'o', color = 'red', markersize = 150)
ctx.add_basemap(ax = ax, source=ctx.providers.NASAGIBS.ViirsEarthAtNight2012)
city geometry
0 Wasserkuppe POINT (1106053.829 6532916.278)
C:\Users\mm\anaconda3\lib\site-packages\contextily\tile.py:632: UserWarning: The inferred zoom level of 9 is not valid for the current tile provider (valid zooms: 1 - 8).
warnings.warn(msg)

wasserkuppe_df = deutschland_df.query(('plz == "36129"'))
wasserkuppe_df = wasserkuppe_df.to_crs(epsg=3857)
df = pd.DataFrame({'city': ['Wasserkuppe'],
'latitude': [50.49768412],
'longitude': [9.9358506]})
gdf = gpd.GeoDataFrame(df.drop(['latitude', 'longitude'], axis=1),
crs = {'init': 'epsg:4326'},
geometry = [shapely.geometry.Point(xy)
for xy in zip(df.longitude, df.latitude)])
gdf = gdf.to_crs(epsg = 3857)
print(gdf)
fig = plt.figure(figsize = (15,15))
ax = plt.subplot()
ax.text(x = 1106053.829 - 2700, y = 6532916.278 + 515, s ='Messstelle Wasserkuppe', size = 18, color = 'white')
wasserkuppe_df = wasserkuppe_df.plot(color='none',edgecolor='gray', linewidth=3, ax = ax)
ax.set_axis_off()
gdf.plot(ax = wasserkuppe_df, marker = 'o', color = 'red', markersize = 150)
ctx.add_basemap(ax = ax, source=ctx.providers.NASAGIBS.ViirsEarthAtNight2012)
city geometry
0 Wasserkuppe POINT (1106053.829 6532916.278)
C:\Users\mm\anaconda3\lib\site-packages\contextily\tile.py:632: UserWarning: The inferred zoom level of 13 is not valid for the current tile provider (valid zooms: 1 - 8).
warnings.warn(msg)
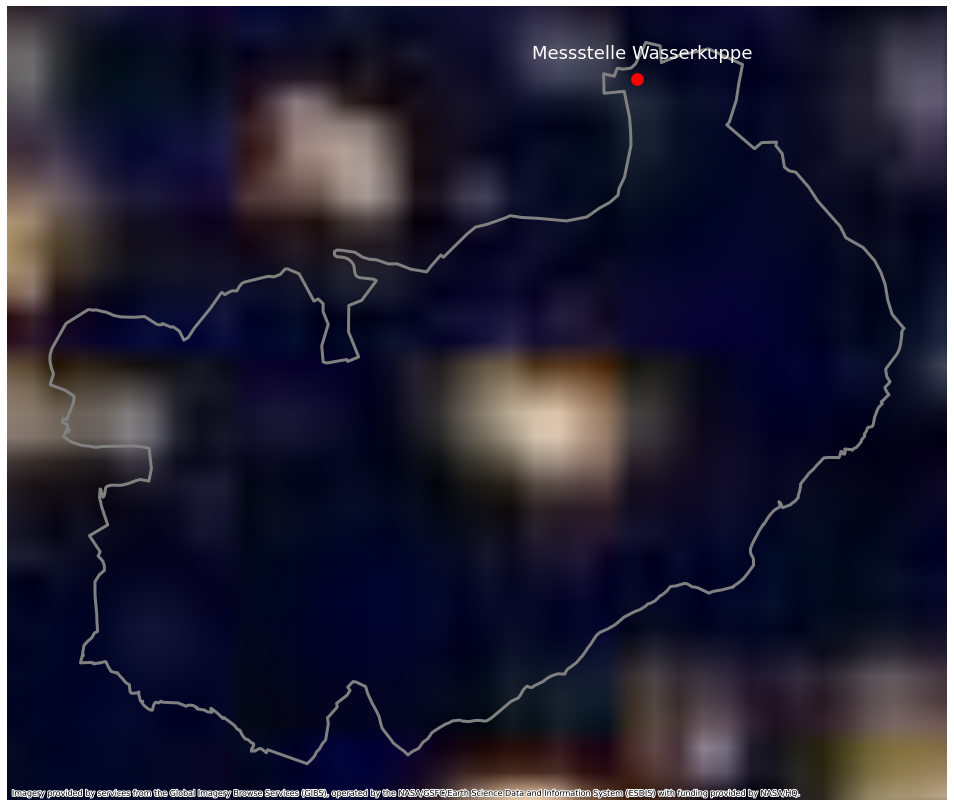
Die verschiedenen Zoomlevel um die Region der Messstelle zeigen wenige Lichter bei Nacht. Hier kann man eine ländliche Region erkennen. Das bedeutet der Datensatz sollte geringe anthropogen Einflüsse der näheren Umgebung haben.
Verarbeitung und Vorverarbeitung vom Datensatz
In diesem Abschnitt wird der Datensatz bearbeitet. Die Daten befinden sich noch im Rohzustand, für eine weitere Verarbeitung, werden sie in bestimmte Formate umgewandelt. Anschließend analysieren wir die Messdaten mit Python. Für die Umsetzung wird das Pandas Framework genutzt. Hauptbestandteil ist die Klasse DataFrame, mit der sich zweidimensionale Tabellen, die aus Zeilen und Spalten bestehen, aufbereiten und umarbeiten lassen. Die Datei messwerte.txt liefert Hinweise, wie die Datei in Python geladen werden soll. Deutschland verwendet ein Komma (,) als Dezimaltrennzeichen. Die meisten europäischen Länder, trennen mit ‚;“ anstatt ‚,‘ und das Dezimaltrennzeichen ist ‚,‘ statt ‚.‘
Datum;Zeit;Kohlendioxid (CO2)[mg/m³];Temperatur[°C];Luftdruck[hPa]
01.12.2019;01:00;867;-3,5;1023
01.12.2019;02:00;885;-3,6;1023
Die Rohdaten stellen folgenden Aufgaben:
Der Datentyp muss von Objekt in Zahl umwgewandelt werden. Die Datumspalte und Zeitspalte in ein Datumsformat bringen („%d-%m-%y %H:%M“).
Die pandas Bibliothek wird geladen und mit mit pd abgekürzt.
import pandas as pd
Die Messdaten einlesen (pd.read_csv) und die Zellen mit ‚;‘ trennen. Dezimaltrennzeichen ‚,‘ ( sep=‘;‘ , decimal=‘,‘).
df_wasserkuppe = pd.read_csv('daten/messwerte_wasserkuppe.txt', sep = ';' , decimal = ',')
Die head-Methode liefert eine Übersicht über die ersten fünf Zeilen.
df_wasserkuppe.head()
| Datum | Zeit | Kohlendioxid (CO2)[mg/m³] | Temperatur[°C] | Luftdruck[hPa] | Windgeschwindigkeit[m/s] | Windrichtung[Grad] | Niederschlag[mm/30min] | Globalstrahlung[W/m²] | |
|---|---|---|---|---|---|---|---|---|---|
| 0 | 05.07.2000 | 01:00 | - | 9,7 | - | 12,6 | - | - | 1 |
| 1 | 05.07.2000 | 02:00 | - | 9,8 | - | 10,8 | - | - | 1 |
| 2 | 05.07.2000 | 03:00 | - | 9,7 | - | 11,0 | - | - | 1 |
| 3 | 05.07.2000 | 04:00 | - | 9,4 | - | 12,8 | - | - | 1 |
| 4 | 05.07.2000 | 05:00 | - | 8,8 | - | 12,6 | - | - | 1 |
Beim Einlesen von Daten versucht Pandas, die Daten automatisch in ein Zahlenformat (Integer oder Floats) zu konvertieren. Mit df.dtypes erhalten wir den entsprechenden Datentyp. Für die Messparameter und das Datum ist das nicht gelungen. Für die Verarbeitungsschritte, die uns noch bevorstehen, ist dieses Format ungeeignet.
df_wasserkuppe.dtypes
Datum object
Zeit object
Kohlendioxid (CO2)[mg/m³] object
Temperatur[°C] object
Luftdruck[hPa] object
Windgeschwindigkeit[m/s] object
Windrichtung[Grad] object
Niederschlag[mm/30min] object
Globalstrahlung[W/m²] object
dtype: object
Die Dezimaltrennzeichen in Spalte Temperatur[°C] ‘,’ mit ‘.’ tauschen und erstelle eine neue Spalte Temperatur (df[‘Temperatur’]). (x.replace)
df_wasserkuppe['Temperatur'] = [x.replace(',' , '.') for x in df_wasserkuppe['Temperatur[°C]']]
df_wasserkuppe.head()
| Datum | Zeit | Kohlendioxid (CO2)[mg/m³] | Temperatur[°C] | Luftdruck[hPa] | Windgeschwindigkeit[m/s] | Windrichtung[Grad] | Niederschlag[mm/30min] | Globalstrahlung[W/m²] | Temperatur | |
|---|---|---|---|---|---|---|---|---|---|---|
| 0 | 05.07.2000 | 01:00 | - | 9,7 | - | 12,6 | - | - | 1 | 9.7 |
| 1 | 05.07.2000 | 02:00 | - | 9,8 | - | 10,8 | - | - | 1 | 9.8 |
| 2 | 05.07.2000 | 03:00 | - | 9,7 | - | 11,0 | - | - | 1 | 9.7 |
| 3 | 05.07.2000 | 04:00 | - | 9,4 | - | 12,8 | - | - | 1 | 9.4 |
| 4 | 05.07.2000 | 05:00 | - | 8,8 | - | 12,6 | - | - | 1 | 8.8 |
Die Datenreihe Luftdruck[hPa], Temperatur und Kohlendioxid (CO2)[mg/m³] von object zu float umwandeln, und erstelle eine neue Spalten namens Luftdruck, Temperatur und Kohlendioxid. (pd.to_numeric) Der Parameter errors=’coerce’ wandelt ‘-‘ und andere Parsingfehler zu NaN (Not a Number) um.
Pandas-Operationen wie to_numeric arbeiten standardmäßig nicht “in-place”. Deswegen werden die Ergebnisse, einer neuen Spalte zugewiesen.
df_wasserkuppe['Luftdruck'] = pd.to_numeric(df_wasserkuppe['Luftdruck[hPa]'], errors = 'coerce')
df_wasserkuppe['Temperatur'] = pd.to_numeric(df_wasserkuppe['Temperatur'], errors = 'coerce')
df_wasserkuppe['Kohlendioxid'] = pd.to_numeric(df_wasserkuppe['Kohlendioxid (CO2)[mg/m³]'], errors = 'coerce')
df_wasserkuppe.head()
| Datum | Zeit | Kohlendioxid (CO2)[mg/m³] | Temperatur[°C] | Luftdruck[hPa] | Windgeschwindigkeit[m/s] | Windrichtung[Grad] | Niederschlag[mm/30min] | Globalstrahlung[W/m²] | Temperatur | Luftdruck | Kohlendioxid | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 0 | 05.07.2000 | 01:00 | - | 9,7 | - | 12,6 | - | - | 1 | 9.7 | NaN | NaN |
| 1 | 05.07.2000 | 02:00 | - | 9,8 | - | 10,8 | - | - | 1 | 9.8 | NaN | NaN |
| 2 | 05.07.2000 | 03:00 | - | 9,7 | - | 11,0 | - | - | 1 | 9.7 | NaN | NaN |
| 3 | 05.07.2000 | 04:00 | - | 9,4 | - | 12,8 | - | - | 1 | 9.4 | NaN | NaN |
| 4 | 05.07.2000 | 05:00 | - | 8,8 | - | 12,6 | - | - | 1 | 8.8 | NaN | NaN |
df_wasserkuppe.tail()
| Datum | Zeit | Kohlendioxid (CO2)[mg/m³] | Temperatur[°C] | Luftdruck[hPa] | Windgeschwindigkeit[m/s] | Windrichtung[Grad] | Niederschlag[mm/30min] | Globalstrahlung[W/m²] | Temperatur | Luftdruck | Kohlendioxid | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 174595 | 04.06.2020 | 20:00 | 735 | 8,8 | 994 | 4,9 | - | 0,0 | 18 | 8.8 | 994.0 | 735.0 |
| 174596 | 04.06.2020 | 21:00 | 737 | 8,8 | 995 | 5,4 | - | - | 3 | 8.8 | 995.0 | 737.0 |
| 174597 | 04.06.2020 | 22:00 | 739 | 8,8 | 995 | 5,9 | - | 0,4 | 1 | 8.8 | 995.0 | 739.0 |
| 174598 | 04.06.2020 | 23:00 | 740 | 7,6 | 995 | 7,4 | - | 0,2 | 1 | 7.6 | 995.0 | 740.0 |
| 174599 | 04.06.2020 | 24:00 | 737 | 6,5 | 995 | 6,6 | - | 0,0 | 1 | 6.5 | 995.0 | 737.0 |
df_wasserkuppe.dtypes
Datum object
Zeit object
Kohlendioxid (CO2)[mg/m³] object
Temperatur[°C] object
Luftdruck[hPa] object
Windgeschwindigkeit[m/s] object
Windrichtung[Grad] object
Niederschlag[mm/30min] object
Globalstrahlung[W/m²] object
Temperatur float64
Luftdruck float64
Kohlendioxid float64
dtype: object
Für die weitere Datenverarbeitung, zum Beispiel für FP Prophet, wird ein bestimmtes Datumsformat benötigt. Zur ‘Zeit’spalte wird “:00” hinzugeügt, ohne Sekundenformat gibt es eine Fehlermeldung. 5
Prophet ist eine Open-Source-Software, die vom Core Data Science-Team von Facebook veröffentlicht wurde. Prophet ist für die Prognose von Zeitreihendaten geeignet.
df_wasserkuppe['Sekundenformat'] = df_wasserkuppe['Zeit'] + ':00'
Die Pandas-Funktion to_datetime wird genutzt, um datumsspezifische Operationen durchführen zu können.
df_wasserkuppe['DatumYDM'] = pd.to_datetime(df_wasserkuppe.Datum)
Pandas wird informiert, dass die zu lesenden Werte nacheinander Angaben zum Tag, Monat, Jahr beinhalten.
df_wasserkuppe["DatumMDY"] = df_wasserkuppe["DatumYDM"].dt.strftime("%d-%m-%y")
Die Spalte Sekundenformat in 0 Tage 01:00:00 wird umgewandelt. (zählt Stunden bis 24 und beginnt bei 0 Tage)
df_wasserkuppe['Stundenzaehler'] = pd.to_timedelta(df_wasserkuppe.Sekundenformat)
Zur Spalte DatumMDY die Spalte Stundenzaehler addiert = 2019-12-01 01:00:00
df_wasserkuppe['DatumStundenzaehler'] = pd.to_datetime(df_wasserkuppe.DatumMDY) + pd.to_timedelta(df_wasserkuppe.Stundenzaehler)
Das Datumsformat wird in 01-12-2019 01:00 umgwandelt
df_wasserkuppe["DatumFinal"] = df_wasserkuppe["DatumStundenzaehler"].dt.strftime("%d-%m-%y %H:%M")
Die folgenden Spalten werden gelöscht:
df_wasserkuppe = df_wasserkuppe.drop(columns = ['Datum', 'Zeit','Sekundenformat','Kohlendioxid (CO2)[mg/m³]','Temperatur[°C]','Luftdruck[hPa]','DatumYDM','DatumMDY','Stundenzaehler','DatumStundenzaehler'])
df_wasserkuppe = df_wasserkuppe.drop(columns=['Windgeschwindigkeit[m/s]', 'Windrichtung[Grad]','Niederschlag[mm/30min]','Globalstrahlung[W/m²]'])
Die Spalte DatumFinal in Datum umbenennen.
df_wasserkuppe = df_wasserkuppe.rename(columns={'DatumFinal' : 'Datum'})
Die Spalte Datum als Index setzen, dadurch werden die Vorzüge der Datumsklasse genutzt.
df_wasserkuppe = df_wasserkuppe.set_index('Datum')
Das Ergebnis: Das Datum wurde als nutzbares Datumsformat umgewandelt. Die Temperatur, Luftdruck und Kohlendioxid sind im Zahlenformat und NaN Werte für fehlende Daten.
df_wasserkuppe.head()
| Temperatur | Luftdruck | Kohlendioxid | |
|---|---|---|---|
| Datum | |||
| 05-07-00 01:00 | 9.7 | NaN | NaN |
| 05-07-00 02:00 | 9.8 | NaN | NaN |
| 05-07-00 03:00 | 9.7 | NaN | NaN |
| 05-07-00 04:00 | 9.4 | NaN | NaN |
| 05-07-00 05:00 | 8.8 | NaN | NaN |
df_wasserkuppe.dtypes
Temperatur float64
Luftdruck float64
Kohlendioxid float64
dtype: object
df_wasserkuppe.info()
<class 'pandas.core.frame.DataFrame'>
DatetimeIndex: 174600 entries, 2000-05-07 01:00:00 to 2020-05-06 00:00:00
Data columns (total 4 columns):
# Column Non-Null Count Dtype
--- ------ -------------- -----
0 Datum 174600 non-null object
1 Temperatur 173564 non-null float64
2 Luftdruck 76646 non-null float64
3 Kohlendioxid 154136 non-null float64
dtypes: float64(3), object(1)
memory usage: 6.7+ MB
Zusammenfassung:
df_wasserkuppe['Temperatur'] = [x.replace(',', '.') for x in df_wasserkuppe['Temperatur[°C]']]
df_wasserkuppe['Luftdruck'] = pd.to_numeric(df_wasserkuppe['Luftdruck[hPa]'], errors='coerce')
df_wasserkuppe['Temperatur'] = pd.to_numeric(df_wasserkuppe['Temperatur'], errors='coerce')
df_wasserkuppe['Kohlendioxid'] = pd.to_numeric(df_wasserkuppe['Kohlendioxid (CO2)[mg/m³]'], errors='coerce')
df_wasserkuppe['Sekundenformat'] = df_wasserkuppe['Zeit'] + ':00'
df_wasserkuppe['DatumYDM'] = pd.to_datetime(df_wasserkuppe.Datum)
df_wasserkuppe["DatumMDY"] = df_wasserkuppe["DatumYDM"].dt.strftime("%d-%m-%y")
df_wasserkuppe['Stundenzaehler'] = pd.to_timedelta(df_wasserkuppe.Sekundenformat)
df_wasserkuppe['DatumStundenzaehler'] = pd.to_datetime(df_wasserkuppe.DatumMDY) + pd.to_timedelta(df_wasserkuppe.Stundenzaehler)
df_wasserkuppe["DatumFinal"] = df_wasserkuppe["DatumStundenzaehler"].dt.strftime("%d-%m-%y %H:%M")
df_wasserkuppe = df_wasserkuppe.drop(columns=['Datum', 'Zeit','Sekundenformat','Kohlendioxid (CO2)[mg/m³]','Temperatur[°C]','Luftdruck[hPa]','DatumYDM','DatumMDY','Stundenzaehler','DatumStundenzaehler'])
df_wasserkuppe = df_wasserkuppe.drop(columns=['Windgeschwindigkeit[m/s]', 'Windrichtung[Grad]','Niederschlag[mm/30min]','Globalstrahlung[W/m²]'])
df_wasserkuppe = df_wasserkuppe.rename(columns={'DatumFinal': 'Datum'})
df_wasserkuppe = df_wasserkuppe.set_index('Datum')
df_wasserkuppe.head()
Die Ergebnisse als csv speichern.
df_wasserkuppe.to_csv('daten/wasserkuppe.csv')
Umrechnung $𝑚𝑔/𝑚^3$ in ppm
Der $CO_2$-Gehalt in der Luft wird in parts per million (Anteile pro Million), kurz ppm, oder in Prozent (%), beziehungsweise Volumenprozent (Vol.-%) angegeben. Zu Beginn der Industrialisierung, um 1750 lag die $CO_2$-Konzentration bei 278 ppm.6 7 Diese historischen Daten sind in ppm, die Messtelle gibt die Kohlendioxidangaben in $𝑚𝑔/𝑚^3$ an. Um die Massenkonzentrationen und Volumenmischungsverhältnisse besser vergleichen zu können, werden sie in diesem Abschnitt umgewandelt. Die Angaben als Massenkonzentrationen in $𝑚𝑔/𝑚^3$ gelten nur für die bestimmten Bedingungen von Druck und Temperatur. Der Befehl df_wasserkuppe.info() liefert uns das maximal 76646 Werte ppm berechnen könnten. Da nur für 76646 Luftdruckwerte vorhanden sind.
df_wasserkuppe = pd.read_csv('daten/wasserkuppe.csv')
df_wasserkuppe.index = pd.to_datetime(df_wasserkuppe.Datum)
df_wasserkuppedrop = df_wasserkuppe.dropna()
df_wasserkuppedrop = df_wasserkuppedrop.drop(columns=['Datum'])
df_wasserkuppedrop
| Temperatur | Luftdruck | Kohlendioxid | |
|---|---|---|---|
| Datum | |||
| 2011-01-09 12:00:00 | 13.4 | 1014.0 | 724.0 |
| 2011-01-09 13:00:00 | 14.6 | 1014.0 | 726.0 |
| 2011-01-09 14:00:00 | 15.6 | 1014.0 | 729.0 |
| 2011-01-09 15:00:00 | 15.6 | 1013.0 | 720.0 |
| 2011-01-09 16:00:00 | 15.6 | 1013.0 | 721.0 |
| ... | ... | ... | ... |
| 2020-04-06 20:00:00 | 8.8 | 994.0 | 735.0 |
| 2020-04-06 21:00:00 | 8.8 | 995.0 | 737.0 |
| 2020-04-06 22:00:00 | 8.8 | 995.0 | 739.0 |
| 2020-04-06 23:00:00 | 7.6 | 995.0 | 740.0 |
| 2020-05-06 00:00:00 | 6.5 | 995.0 | 737.0 |
75072 rows × 3 columns
Umrechnungsformel
mg = 0.1ppm1mol/((8.31447*(t+273.15))/p)
ppm = 10mg2/mol((8.31447*(t+273.15))/p)
mg2…ist die Massenkonzentration des Messwertes Kohlendioxid in mg/m3
p…ist der Bezugsdruck. Der Normdruck wäre 1013,25 mbar.
mol…die molare Masse von Kohlendioxid in g/mol: 44,01 g/mol
10 ergibt sich als Umrechnungsfaktor, da keine konsistenten Einheiten verwendet werden8
R ist die Universelle Gaskonstante = 8,314472 J/(K·mol)
t= 13.4
p=1013.25
mol=44.01
mg2=724
ppm = 10*mg2/mol*((8.31447*(t+273.15))/p)
ppm
386.8170144884977
Berechnung der Werte 2011-01-09 12:00:00 und 2020-05-06 00:00:00
t= 6.5
p=995
mol=44.01
mg2=737
ppm = 10*mg2/mol*((8.31447*(t+273.15))/p)
ppm
391.32936019874427
t= 13.4
p=1014
mol=44.01
mg2=724
ppm = 10*mg2/mol*((8.31447*(t+273.15))/p)
ppm
386.5309072292606
t = df_wasserkuppedrop['Temperatur']
p = df_wasserkuppedrop['Luftdruck']
mol = 44.01
mg2 = df_wasserkuppedrop['Kohlendioxid']
df_wasserkuppedrop['ppm'] = 10*mg2/mol*((8.31447*(t+273.15))/p)
df_wasserkuppedrop['ppm']
Datum
2011-01-09 12:00:00 386.530907
2011-01-09 13:00:00 389.221839
2011-01-09 14:00:00 392.188422
2011-01-09 15:00:00 387.728965
2011-01-09 16:00:00 388.267478
...
2020-04-06 20:00:00 393.873041
2020-04-06 21:00:00 394.547875
2020-04-06 22:00:00 395.618561
2020-04-06 23:00:00 394.467844
2020-05-06 00:00:00 391.329360
Name: ppm, Length: 75072, dtype: float64
df_wasserkuppedrop
| Temperatur | Luftdruck | Kohlendioxid | ppm | |
|---|---|---|---|---|
| Datum | ||||
| 2011-01-09 12:00:00 | 13.4 | 1014.0 | 724.0 | 386.530907 |
| 2011-01-09 13:00:00 | 14.6 | 1014.0 | 726.0 | 389.221839 |
| 2011-01-09 14:00:00 | 15.6 | 1014.0 | 729.0 | 392.188422 |
| 2011-01-09 15:00:00 | 15.6 | 1013.0 | 720.0 | 387.728965 |
| 2011-01-09 16:00:00 | 15.6 | 1013.0 | 721.0 | 388.267478 |
| ... | ... | ... | ... | ... |
| 2020-04-06 20:00:00 | 8.8 | 994.0 | 735.0 | 393.873041 |
| 2020-04-06 21:00:00 | 8.8 | 995.0 | 737.0 | 394.547875 |
| 2020-04-06 22:00:00 | 8.8 | 995.0 | 739.0 | 395.618561 |
| 2020-04-06 23:00:00 | 7.6 | 995.0 | 740.0 | 394.467844 |
| 2020-05-06 00:00:00 | 6.5 | 995.0 | 737.0 | 391.329360 |
75072 rows × 4 columns
dfco2m = df_wasserkuppedrop.resample('M').mean()
dfco2m
| Temperatur | Luftdruck | Kohlendioxid | ppm | |
|---|---|---|---|---|
| Datum | ||||
| 2011-01-31 | 9.861905 | 1018.083333 | 718.535714 | 377.267934 |
| 2011-02-28 | 10.933333 | 1015.166667 | 718.979167 | 380.087965 |
| 2011-03-31 | 10.738542 | 1012.093750 | 723.416667 | 383.434028 |
| 2011-04-30 | 10.977660 | 1008.351064 | 724.648936 | 385.891135 |
| 2011-05-31 | 8.386458 | 1008.500000 | 723.479167 | 381.627605 |
| ... | ... | ... | ... | ... |
| 2020-08-31 | 5.670833 | 1020.233333 | 751.100000 | 387.711256 |
| 2020-09-30 | 7.174167 | 1014.941667 | 745.800000 | 389.088071 |
| 2020-10-31 | 5.693333 | 1009.225000 | 741.425000 | 386.948444 |
| 2020-11-30 | 2.715833 | 1012.291667 | 745.200000 | 383.644441 |
| 2020-12-31 | 2.384167 | 1013.800000 | 746.466667 | 383.237839 |
120 rows × 4 columns
import matplotlib.pyplot as plt
import matplotlib.style as style
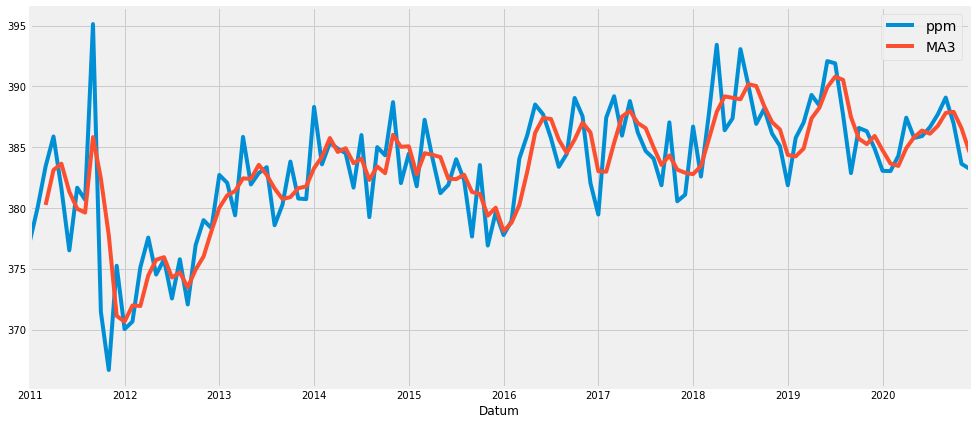
dfco2m['ppm'].plot(label = 'ppm', figsize=(15,7))
dfco2m['MA3'] = dfco2m['ppm'].rolling(3).mean()
dfco2m['MA3'].plot(label='MA3')
style.use('fivethirtyeight')
plt.legend()
<matplotlib.legend.Legend at 0x172fbda4988>
Streudiagramme
import matplotlib.pyplot as plt
import numpy as np
from pandas.plotting import scatter_matrix
#df['logarithm'] = np.log(df['Temperatur'])
#dfny = df.dropna()
#scatter_matrix(df['logarithm'])
#df.plot.scatter(df, loglog=True)
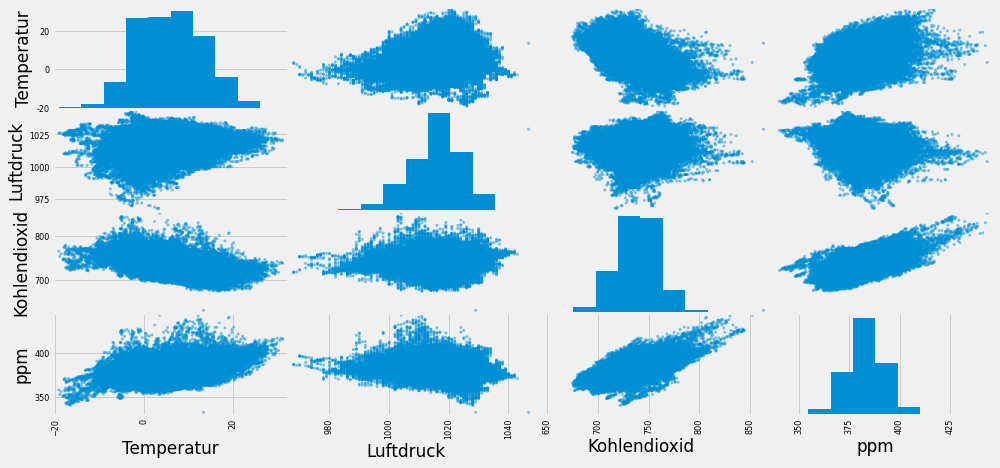
scatter_matrix(df_wasserkuppedrop, figsize=(15,7))
array([[<AxesSubplot:xlabel='Temperatur', ylabel='Temperatur'>,
<AxesSubplot:xlabel='Luftdruck', ylabel='Temperatur'>,
<AxesSubplot:xlabel='Kohlendioxid', ylabel='Temperatur'>,
<AxesSubplot:xlabel='ppm', ylabel='Temperatur'>],
[<AxesSubplot:xlabel='Temperatur', ylabel='Luftdruck'>,
<AxesSubplot:xlabel='Luftdruck', ylabel='Luftdruck'>,
<AxesSubplot:xlabel='Kohlendioxid', ylabel='Luftdruck'>,
<AxesSubplot:xlabel='ppm', ylabel='Luftdruck'>],
[<AxesSubplot:xlabel='Temperatur', ylabel='Kohlendioxid'>,
<AxesSubplot:xlabel='Luftdruck', ylabel='Kohlendioxid'>,
<AxesSubplot:xlabel='Kohlendioxid', ylabel='Kohlendioxid'>,
<AxesSubplot:xlabel='ppm', ylabel='Kohlendioxid'>],
[<AxesSubplot:xlabel='Temperatur', ylabel='ppm'>,
<AxesSubplot:xlabel='Luftdruck', ylabel='ppm'>,
<AxesSubplot:xlabel='Kohlendioxid', ylabel='ppm'>,
<AxesSubplot:xlabel='ppm', ylabel='ppm'>]], dtype=object)
dfco2m = dfco2m.drop(columns = ['MA3'])
dfco2m
| Temperatur | Luftdruck | Kohlendioxid | ppm | |
|---|---|---|---|---|
| Datum | ||||
| 2011-01-31 | 9.861905 | 1018.083333 | 718.535714 | 377.267934 |
| 2011-02-28 | 10.933333 | 1015.166667 | 718.979167 | 380.087965 |
| 2011-03-31 | 10.738542 | 1012.093750 | 723.416667 | 383.434028 |
| 2011-04-30 | 10.977660 | 1008.351064 | 724.648936 | 385.891135 |
| 2011-05-31 | 8.386458 | 1008.500000 | 723.479167 | 381.627605 |
| ... | ... | ... | ... | ... |
| 2020-08-31 | 5.670833 | 1020.233333 | 751.100000 | 387.711256 |
| 2020-09-30 | 7.174167 | 1014.941667 | 745.800000 | 389.088071 |
| 2020-10-31 | 5.693333 | 1009.225000 | 741.425000 | 386.948444 |
| 2020-11-30 | 2.715833 | 1012.291667 | 745.200000 | 383.644441 |
| 2020-12-31 | 2.384167 | 1013.800000 | 746.466667 | 383.237839 |
120 rows × 4 columns
import matplotlib.pyplot as plt
import numpy as np
from pandas.plotting import scatter_matrix
#df['logarithm'] = np.log(df['Temperatur'])
#dfny = df.dropna()
#scatter_matrix(df['logarithm'])
#df.plot.scatter(df, loglog=True)
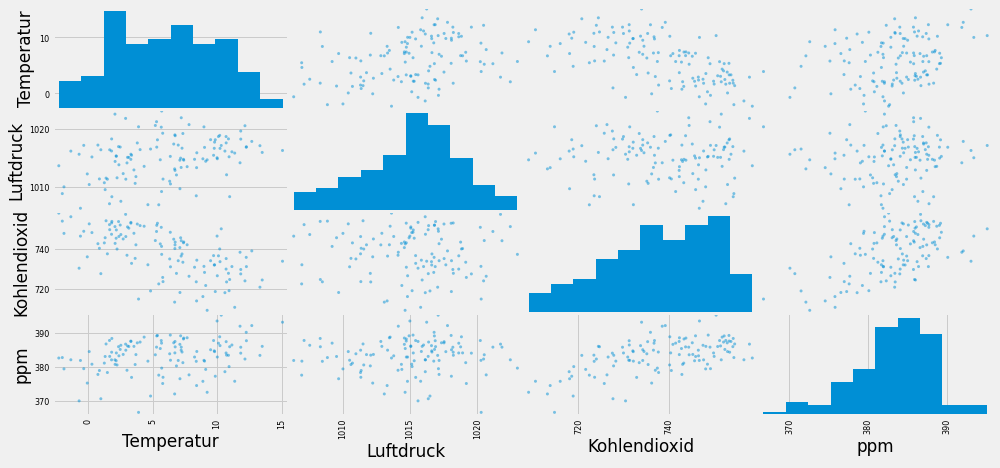
scatter_matrix(dfco2m , figsize=(15,7))
array([[<AxesSubplot:xlabel='Temperatur', ylabel='Temperatur'>,
<AxesSubplot:xlabel='Luftdruck', ylabel='Temperatur'>,
<AxesSubplot:xlabel='Kohlendioxid', ylabel='Temperatur'>,
<AxesSubplot:xlabel='ppm', ylabel='Temperatur'>],
[<AxesSubplot:xlabel='Temperatur', ylabel='Luftdruck'>,
<AxesSubplot:xlabel='Luftdruck', ylabel='Luftdruck'>,
<AxesSubplot:xlabel='Kohlendioxid', ylabel='Luftdruck'>,
<AxesSubplot:xlabel='ppm', ylabel='Luftdruck'>],
[<AxesSubplot:xlabel='Temperatur', ylabel='Kohlendioxid'>,
<AxesSubplot:xlabel='Luftdruck', ylabel='Kohlendioxid'>,
<AxesSubplot:xlabel='Kohlendioxid', ylabel='Kohlendioxid'>,
<AxesSubplot:xlabel='ppm', ylabel='Kohlendioxid'>],
[<AxesSubplot:xlabel='Temperatur', ylabel='ppm'>,
<AxesSubplot:xlabel='Luftdruck', ylabel='ppm'>,
<AxesSubplot:xlabel='Kohlendioxid', ylabel='ppm'>,
<AxesSubplot:xlabel='ppm', ylabel='ppm'>]], dtype=object)
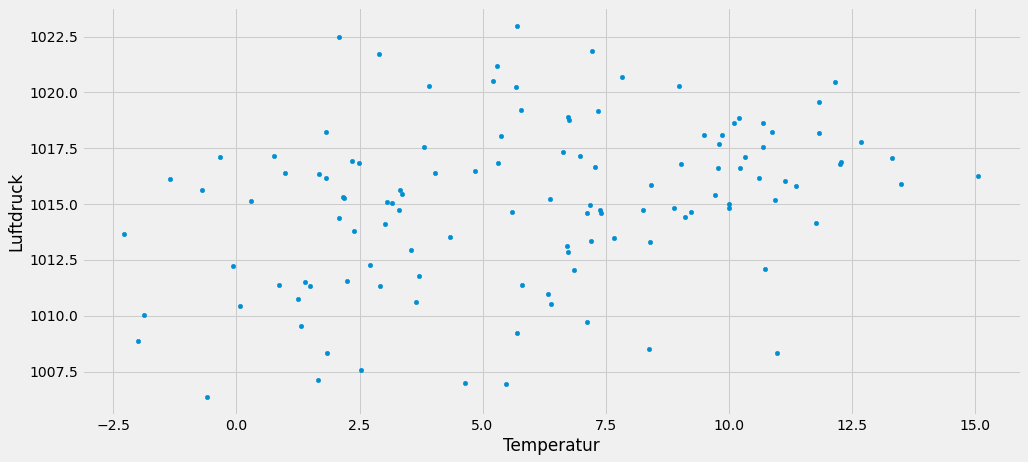
dfco2m.plot.scatter(x='Temperatur', y='Luftdruck', loglog=False, alpha=1, figsize=(15,7))
plt.show()
dfco2m.plot.scatter(x='Temperatur', y='ppm', loglog=False, alpha=1, figsize=(15,7))
plt.show()
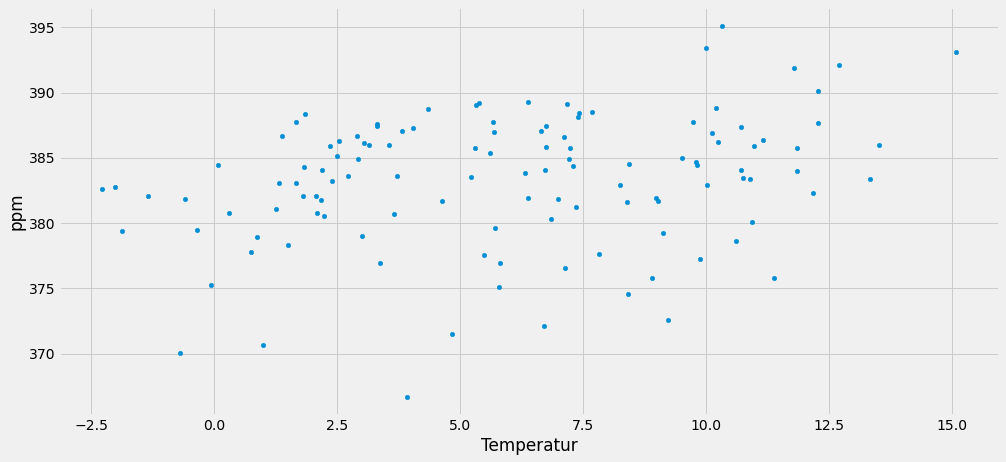
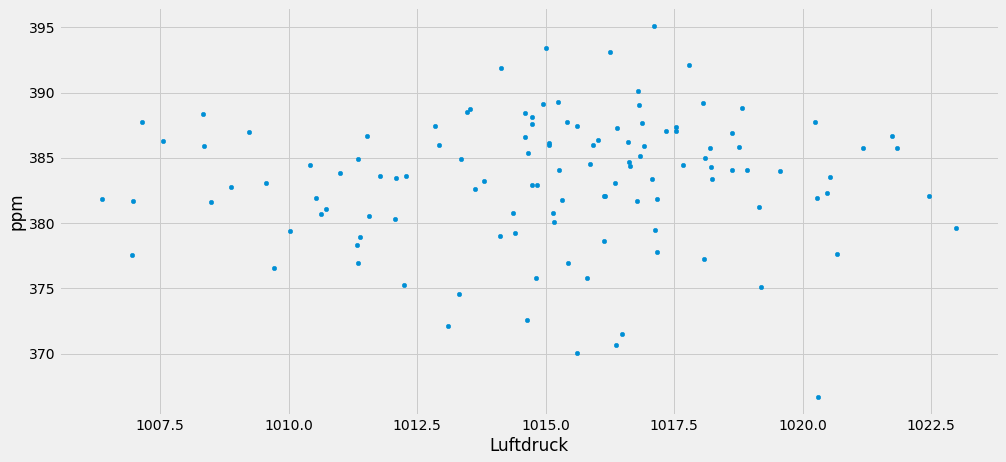
dfco2m.plot.scatter(x='Luftdruck', y='ppm', loglog=False, alpha=1, figsize=(15,7))
plt.show()
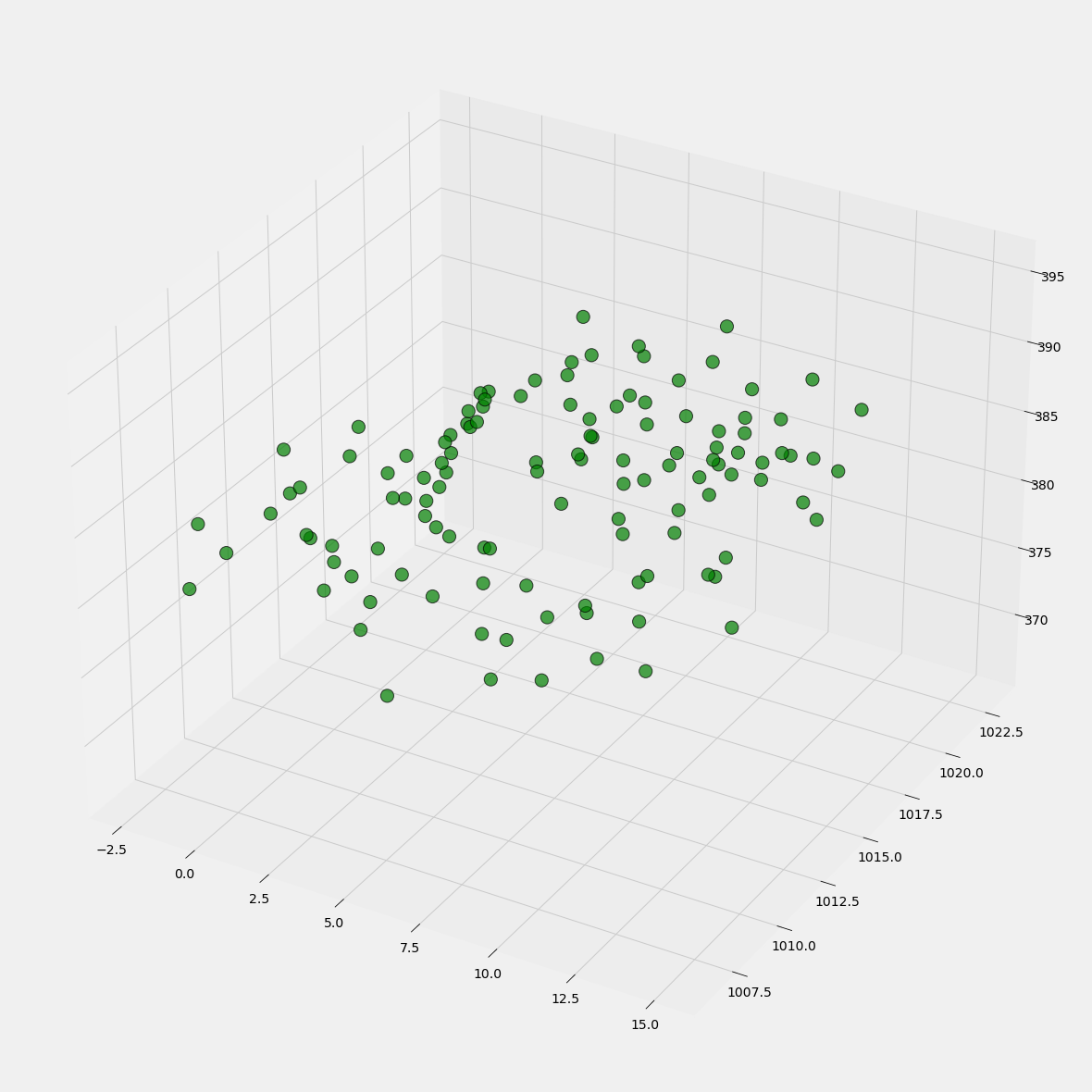
3D Streudiagramm
#https://stackoverflow.com/questions/59232073/scatter-plot-with-3-variables-in-matplotlib
#https://www.advsofteng.com/doc/cdpydoc/threedscatter2.htm Dropline
import matplotlib.pyplot as plt
from mpl_toolkits.mplot3d import Axes3D
import numpy as np
x = np.array(dfco2m['Temperatur'])
y = np.array(dfco2m['Luftdruck'])
z = np.array(dfco2m['ppm'])
fig = plt.figure(figsize=(20, 20))
ax = fig.add_subplot(111, projection='3d')
ax.scatter(x, y, z,
linewidths=1, alpha=.7,
edgecolor='k',
s = 200,
c='green',
)
plt.show()
dfco2m.info()
<class 'pandas.core.frame.DataFrame'>
DatetimeIndex: 120 entries, 2011-01-31 to 2020-12-31
Freq: M
Data columns (total 4 columns):
# Column Non-Null Count Dtype
--- ------ -------------- -----
0 Temperatur 120 non-null float64
1 Luftdruck 120 non-null float64
2 Kohlendioxid 120 non-null float64
3 ppm 120 non-null float64
dtypes: float64(4)
memory usage: 4.7 KB
x.shape
(120,)
y.shape
(120,)
z.shape
(120,)
ToDO: Droplines https://matplotlib.org/devdocs/gallery/mplot3d/stem3d_demo.html
Siehe: https://support.minitab.com/de-de/minitab/19/help-and-how-to/graphs/3d-scatterplot/interpret-the-results/key-results/
Visualisierung der Kohlendioxidmessung
import locale
locale.setlocale(locale.LC_ALL, 'de_DE')
import numpy as np
import matplotlib.pyplot as plt
import matplotlib.style as style
style.use('fivethirtyeight')
from calendar import month_abbr
df_vis = pd.read_csv('daten/wasserkuppe.csv')
df_vis.index = pd.to_datetime(df_vis.Datum)
df_vis
| Datum | Temperatur | Luftdruck | Kohlendioxid | |
|---|---|---|---|---|
| Datum | ||||
| 2000-05-07 01:00:00 | 05-07-00 01:00 | 9.7 | NaN | NaN |
| 2000-05-07 02:00:00 | 05-07-00 02:00 | 9.8 | NaN | NaN |
| 2000-05-07 03:00:00 | 05-07-00 03:00 | 9.7 | NaN | NaN |
| 2000-05-07 04:00:00 | 05-07-00 04:00 | 9.4 | NaN | NaN |
| 2000-05-07 05:00:00 | 05-07-00 05:00 | 8.8 | NaN | NaN |
| ... | ... | ... | ... | ... |
| 2020-04-06 20:00:00 | 04-06-20 20:00 | 8.8 | 994.0 | 735.0 |
| 2020-04-06 21:00:00 | 04-06-20 21:00 | 8.8 | 995.0 | 737.0 |
| 2020-04-06 22:00:00 | 04-06-20 22:00 | 8.8 | 995.0 | 739.0 |
| 2020-04-06 23:00:00 | 04-06-20 23:00 | 7.6 | 995.0 | 740.0 |
| 2020-05-06 00:00:00 | 05-06-20 00:00 | 6.5 | 995.0 | 737.0 |
174600 rows × 4 columns
df_vis = df_vis.resample('M').mean()
df_vis
| Temperatur | Luftdruck | Kohlendioxid | |
|---|---|---|---|
| Datum | |||
| 2000-01-31 | 9.597414 | NaN | NaN |
| 2000-02-29 | 6.987156 | NaN | NaN |
| 2000-03-31 | 5.985321 | NaN | NaN |
| 2000-04-30 | 5.805000 | NaN | NaN |
| 2000-05-31 | 6.943972 | NaN | NaN |
| ... | ... | ... | ... |
| 2020-08-31 | 5.670833 | 1020.233333 | 751.100000 |
| 2020-09-30 | 7.174167 | 1014.941667 | 745.800000 |
| 2020-10-31 | 5.693333 | 1009.225000 | 741.425000 |
| 2020-11-30 | 2.715833 | 1012.291667 | 745.200000 |
| 2020-12-31 | 2.384167 | 1013.800000 | 746.466667 |
252 rows × 3 columns
t = df_vis['Temperatur']
p = df_vis['Luftdruck']
mol = 44.01
mg2 = df_vis['Kohlendioxid']
df_vis['ppm'] = 10*mg2/mol*((8.31447*(t+273.15))/p)
df_vis
| Temperatur | Luftdruck | Kohlendioxid | ppm | |
|---|---|---|---|---|
| Datum | ||||
| 2000-01-31 | 9.597414 | NaN | NaN | NaN |
| 2000-02-29 | 6.987156 | NaN | NaN | NaN |
| 2000-03-31 | 5.985321 | NaN | NaN | NaN |
| 2000-04-30 | 5.805000 | NaN | NaN | NaN |
| 2000-05-31 | 6.943972 | NaN | NaN | NaN |
| ... | ... | ... | ... | ... |
| 2020-08-31 | 5.670833 | 1020.233333 | 751.100000 | 387.798992 |
| 2020-09-30 | 7.174167 | 1014.941667 | 745.800000 | 389.157172 |
| 2020-10-31 | 5.693333 | 1009.225000 | 741.425000 | 387.010451 |
| 2020-11-30 | 2.715833 | 1012.291667 | 745.200000 | 383.661572 |
| 2020-12-31 | 2.384167 | 1013.800000 | 746.466667 | 383.280561 |
252 rows × 4 columns
df_vis = df_vis.drop(columns=['Temperatur','Luftdruck','Kohlendioxid'])
df_vis
| ppm | |
|---|---|
| Datum | |
| 2000-01-31 | NaN |
| 2000-02-29 | NaN |
| 2000-03-31 | NaN |
| 2000-04-30 | NaN |
| 2000-05-31 | NaN |
| ... | ... |
| 2020-08-31 | 387.798992 |
| 2020-09-30 | 389.157172 |
| 2020-10-31 | 387.010451 |
| 2020-11-30 | 383.661572 |
| 2020-12-31 | 383.280561 |
252 rows × 1 columns
Folgender Code war bei der Erstellung hilfreich 9
co2_data = df_vis['2011':'2019']
n_years = co2_data.index.year.max() - co2_data.index.year.min()
z = np.ones((n_years +1 , 12)) * np.min(co2_data.ppm)
for d, y in co2_data.groupby([co2_data.index.year, co2_data.index.month]):
z[co2_data.index.year.max() - d[0], d[1] - 1] = y.mean()[0]
plt.figure(figsize=(10, 14))
plt.pcolor(np.flipud(z), cmap='hot_r')
plt.yticks(np.arange(0, n_years+1)+.5,
range(co2_data.index.year.min(), co2_data.index.year.max()+1));
plt.xticks(np.arange(13)-.5, month_abbr)
plt.xlim((0, 12))
plt.colorbar().set_label('Kohlendioxidmessung in mg/m³ der Messstation Wasserkuppe ')
plt.show()
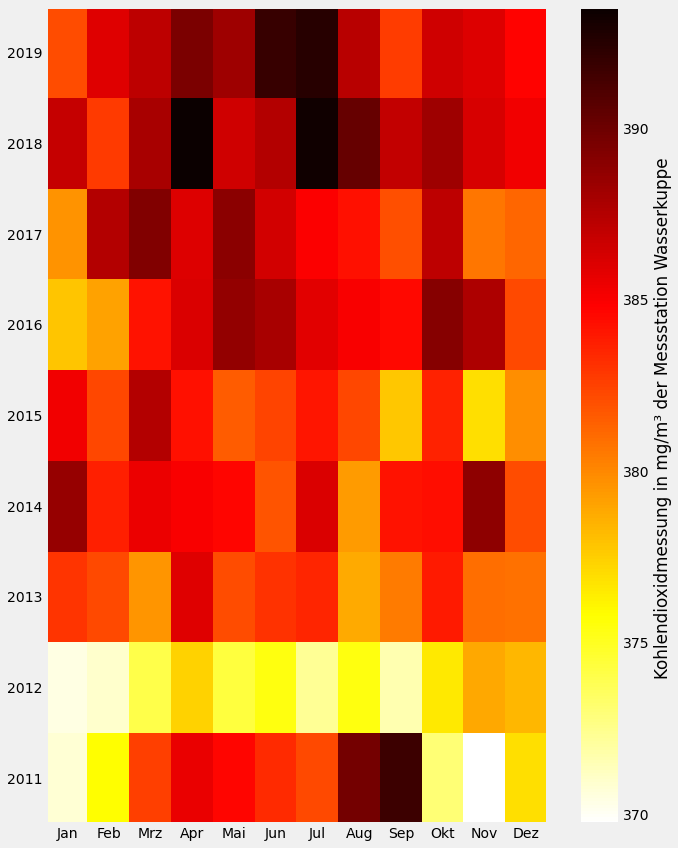
In der Abbildung sind die Kohlendioxidwerte für November 2011 am geringsten und im April 2018 am höchsten. Der Einfluss der Nordhemisphäre dominiert den jährlichen Zyklus der Schwankung der Kohlenstoffdioxidkonzentration, denn dort befinden sich weit größere Landflächen und somit eine größere Biomasse als auf der Südhemisphäre. Die Konzentration ist im Mai auf der Nordhemisphäre am höchsten, da das im Frühling stattfindende Ergrünen zu dieser Zeit beginnt; sie erreicht ihr Minimum im Oktober, wenn die Photosynthese betreibende Biomasse am größten ist.10
Minimale und maximale Werte
Anschließend werden die maximalen und minimalen Werte aufgelistet.
t = pd.to_datetime('11-11-30')
t
df_wasserkuppe_01_02_2002_12_0 = df_vis[(df_vis.index == '2011-11-30')]
df_wasserkuppe_01_02_2002_12_0
| ppm | |
|---|---|
| Datum | |
| 2011-11-30 | 369.717896 |
df_wasserkuppe_01_02_2002_12_0 = df_vis[(df_vis.index == '2018-07-31')]
df_wasserkuppe_01_02_2002_12_0
| ppm | |
|---|---|
| Datum | |
| 2018-07-31 | 393.254659 |
df_vis['ppm'].argmax()
219
df_vis.iloc[[df_vis['ppm'].argmax()]]
| ppm | |
|---|---|
| Datum | |
| 2018-04-30 | 393.527525 |
df_vis.iloc[[df_vis['ppm'].argmin()]]
| ppm | |
|---|---|
| Datum | |
| 2011-11-30 | 369.717896 |
Wird fortgesetzt…
Quellenangaben:
Quellenangaben Sonstiges:
https://stackoverflow.com/questions/51621615/which-geopandas-datasets-maps-are-available
https://github.com/geopandas/geopandas/blob/master/doc/source/gallery/plotting_basemap_background.ipynb
https://geopandas.org/gallery/plotting_basemap_background.html
Webseite: https://www.hlnug.de/themen/luft/luftschadstoffe/kohlendioxid ↩
Jacobi, S. (o.D.). Grundlagen der Luftreinhaltung [Vorlesungsfolien]. Hessisches Landesamt für Naturschutz, Umwelt und Geologie Wiesbaden. https://www.hlnug.de/fileadmin/dokumente/luft/externe_fachveranstaltungen/vorlesungen/jacobi/02_Grundlagen_der_Luftreinhaltung.pdf . Abgerufen am 17. März 2021. ↩
Orduz, J. C. (2020, 7. Januar). Open Data: Germany Maps Viz. Dr. Juan Camilo Orduz. https://juanitorduz.github.io/germany_plots/ ↩
Hattenbach, J. (2012, 6. Dezember). Das neue Bild der Erde - bei Nacht. SciLogs - Wissenschaftsblogs. https://scilogs.spektrum.de/himmelslichter/das-neue-bild-der-erde-bei-nacht/ ↩
Webseite: https://facebook.github.io/prophet/ ↩
Kohlendioxid-Konzentration – Klimawandel. (2019). bildungsserver. https://wiki.bildungsserver.de/klimawandel/index.php/Kohlendioxid-Konzentration ↩
Wikipedia-Autoren. (2007, 16. Mai). Kohlenstoffdioxid in der Erdatmosphäre. Wikipedia. https://de.wikipedia.org/wiki/Kohlenstoffdioxid_in_der_Erdatmosph%C3%A4re ↩
ppm in mg/m3. (2019). NABU Eibelshausen. http://www.nabu-eibelshausen.de/Rechner/ppm.html ↩
Vettigli, G. (2019, 22. April). Visualizing Atmospheric Carbon Dioxide. Dzone.Com. https://dzone.com/articles/visualizing-atmospheric-carbon-dioxide ↩
U.K. (2016, 21. Januar). Florierende Vegetation verstärkt Kohlendioxid-Schwankungen. Max-Planck-Gesellschaft. https://www.mpg.de/9862783/co2-schwankung-vegetation-erderwaermung ↩
